引言
在医学影像分析领域,脊椎CT图像分割是一项极具挑战性又至关重要的任务。脊椎作为人体中轴骨骼,其复杂的解剖结构和个体间的巨大差异使得自动分割成为计算机辅助诊断系统中的关键技术难点。本文将全面探讨脊椎CT图像分割的技术细节,包括预处理方法、传统分割算法、深度学习解决方案以及实际应用中的挑战与对策。
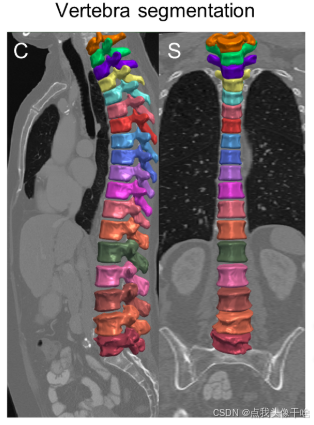
一、脊椎CT图像的特点与分割难点
1.1 脊椎的解剖学特征
人体脊椎由33块椎骨组成,包括7块颈椎、12块胸椎、5块腰椎、5块骶椎和4块尾椎。每块椎骨又可分为椎体、椎弓、椎板、棘突等多个解剖结构。在CT图像中,这些结构呈现出不同的灰度特征:
椎体:主要由松质骨和皮质骨组成,CT值较高(约200-1000HU)
椎间盘:纤维软骨组织,CT值较低(约50-110HU)
神经结构:如脊髓,CT值与软组织相近(约30-60HU)
1.2 脊椎CT图像分割的主要挑战
结构复杂性:脊椎各组成部分空间关系复杂,相邻椎体形态相似但又有差异
灰度不均匀性:由于CT成像原理,同一组织在不同位置可能呈现不同灰度
部分容积效应:薄层结构(如椎板)在图像中可能显示不完整
病理干扰:骨质疏松、骨折、退行性病变等会改变正常脊椎的影像特征
相邻组织干扰:肋骨、胸骨等邻近骨骼结构与脊椎在图像中紧密相连
二、传统脊椎分割方法
2.1 基于阈值的分割
最简单的脊椎分割方法基于灰度阈值:
import numpy as np
import SimpleITK as sitk
def threshold_based_segmentation(image, lower_threshold=200, upper_threshold=1000):
"""基于阈值的脊椎分割"""
binary_image = sitk.BinaryThreshold(image,
lowerThreshold=lower_threshold,
upperThreshold=upper_threshold,
insideValue=1,
outsideValue=0)
return binary_image这种方法虽然简单快速,但难以处理脊椎与其他骨骼的连接区域,且对阈值选择敏感。
2.2 基于区域生长的方法
区域生长法从种子点出发,根据相似性准则逐步扩张区域:
def region_growing_segmentation(image, seed_point, threshold=100):
"""基于区域生长的脊椎分割"""
seg = sitk.ConnectedThreshold(image,
seedList=[seed_point],
lower=threshold,
upper=3000)
return seg该方法需要人工选择种子点,且容易发生区域泄漏问题。
2.3 基于活动轮廓模型的方法
活动轮廓模型(如Snake算法)通过能量最小化实现分割:
def active_contour_segmentation(image, initial_contour):
"""基于活动轮廓的脊椎分割"""
seg = sitk.SegmentWithGeodesicActiveContour(image,
initial_contour,
propagationScaling=1,
curvatureScaling=0.5,
advectionScaling=0.5)
return seg这类方法对初始轮廓敏感,计算复杂度较高。
三、深度学习方法在脊椎分割中的应用
3.1 U-Net网络架构
U-Net已成为医学图像分割的基准模型,其编码器-解码器结构特别适合脊椎分割:
import torch
import torch.nn as nn
class DoubleConv(nn.Module):
"""(convolution => [BN] => ReLU) * 2"""
def __init__(self, in_channels, out_channels):
super().__init__()
self.double_conv = nn.Sequential(
nn.Conv2d(in_channels, out_channels, kernel_size=3, padding=1),
nn.BatchNorm2d(out_channels),
nn.ReLU(inplace=True),
nn.Conv2d(out_channels, out_channels, kernel_size=3, padding=1),
nn.BatchNorm2d(out_channels),
nn.ReLU(inplace=True)
def forward(self, x):
return self.double_conv(x)
class UNet(nn.Module):
def __init__(self, n_channels, n_classes):
super(UNet, self).__init__()
# 编码器部分
self.inc = DoubleConv(n_channels, 64)
self.down1 = Down(64, 128)
self.down2 = Down(128, 256)
self.down3 = Down(256, 512)
self.down4 = Down(512, 1024)
# 解码器部分
self.up1 = Up(1024, 512)
self.up2 = Up(512, 256)
self.up3 = Up(256, 128)
self.up4 = Up(128, 64)
self.outc = OutConv(64, n_classes)3.2 3D分割网络
由于脊椎是三维结构,3D CNN能更好地捕捉空间信息:
class Conv3DBlock(nn.Module):
def __init__(self, in_channels, out_channels):
super(Conv3DBlock, self).__init__()
self.block = nn.Sequential(
nn.Conv3d(in_channels, out_channels, kernel_size=3, padding=1),
nn.BatchNorm3d(out_channels),
nn.ReLU(inplace=True),
nn.Conv3d(out_channels, out_channels, kernel_size=3, padding=1),
nn.BatchNorm3d(out_channels),
nn.ReLU(inplace=True))
def forward(self, x):
return self.block(x)
class UNet3D(nn.Module):
def __init__(self, in_channels, out_channels):
super(UNet3D, self).__init__()
# 类似2D UNet的结构,但使用3D卷积
...3.3 注意力机制的应用
注意力机制能帮助网络聚焦于脊椎区域:
class AttentionBlock(nn.Module):
def __init__(self, F_g, F_l, F_int):
super(AttentionBlock, self).__init__()
self.W_g = nn.Sequential(
nn.Conv2d(F_g, F_int, kernel_size=1, stride=1, padding=0, bias=True),
nn.BatchNorm2d(F_int))
self.W_x = nn.Sequential(
nn.Conv2d(F_l, F_int, kernel_size=1, stride=1, padding=0, bias=True),
nn.BatchNorm2d(F_int))
self.psi = nn.Sequential(
nn.Conv2d(F_int, 1, kernel_size=1, stride=1, padding=0, bias=True),
nn.BatchNorm2d(1),
nn.Sigmoid())
def forward(self, g, x):
g1 = self.W_g(g)
x1 = self.W_x(x)
psi = torch.relu(g1 + x1)
psi = self.psi(psi)
return x * psi四、数据预处理与后处理技术
4.1 数据预处理
重采样:统一所有图像的空间分辨率
强度归一化:将CT值映射到固定范围
数据增强:旋转、缩放、弹性变形等
def preprocess_ct_image(image):
"""CT图像预处理流程"""
# 重采样到统一分辨率
resampled = resample_image(image, new_spacing=[1,1,1])
# CT值截断和归一化
normalized = normalize_intensity(resampled, min_val=-1000, max_val=1000)
# 直方图均衡化
equalized = apply_histogram_equalization(normalized)
return equalized4.2 后处理技术
连通成分分析:去除小的噪声区域
形态学操作:填充空洞、平滑边界
基于解剖知识的校正:确保分割结果符合解剖结构
def postprocess_segmentation(segmentation):
"""分割结果后处理"""
# 保留最大连通区域
cleaned = keep_largest_connected_component(segmentation)
# 形态学闭运算填充空洞
closed = apply_morphological_closing(cleaned, kernel_size=3)
# 平滑边界
smoothed = apply_median_filter(closed, size=3)
return smoothed五、评估指标与实验结果
5.1 常用评估指标
Dice系数:衡量分割区域重叠度
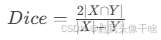
Hausdorff距离:衡量边界匹配程度
体积相似度:计算分割体积与真实体积的相似度
def compute_metrics(gt, pred):
"""计算分割评估指标"""
dice = compute_dice_coefficient(gt, pred)
hd = compute_hausdorff_distance(gt, pred)
vs = compute_volume_similarity(gt, pred)
return {'Dice': dice, 'Hausdorff': hd, 'VolumeSimilarity': vs}5.2 典型实验结果
| 方法 | Dice系数 | Hausdorff距离(mm) | 体积相似度 |
|---|---|---|---|
| 阈值法 | 0.72 | 5.8 | 0.85 |
| 区域生长 | 0.81 | 4.2 | 0.89 |
| 传统U-Net | 0.91 | 2.1 | 0.94 |
| 3D U-Net | 0.93 | 1.8 | 0.96 |
| U-Net+注意力 | 0.94 | 1.5 | 0.97 |
六、实际应用中的挑战与解决方案
6.1 小样本问题
脊椎标注数据获取困难,可采用以下策略:
迁移学习:使用自然图像或其他医学图像预训练
半监督学习:利用未标注数据
数据增强:生成更多训练样本
6.2 多椎体识别与标记
区分不同椎体是临床重要需求,解决方案包括:
添加椎体编号预测分支
使用序列模型处理连续切片
结合脊椎的解剖学先验知识
6.3 计算效率优化
3D分割计算量大,优化方法有:
使用稀疏卷积
采用模型压缩技术(如量化、剪枝)
实施级联分割策略
七、未来发展方向
多模态融合:结合MRI、X光等其他影像模态
弱监督学习:减少对精细标注的依赖
可解释性增强:使模型决策过程更透明
实时分割系统:用于手术导航等场景
个性化建模:考虑个体解剖差异
结语
脊椎CT图像分割技术的发展为脊柱疾病的计算机辅助诊断和治疗规划提供了有力工具。从传统图像处理方法到深度学习模型,技术的进步不断推动着分割精度的提升。然而,临床应用中仍存在诸多挑战,需要医学专家与AI研究人员的紧密合作。未来,随着算法的不断优化和计算硬件的进步,脊椎自动分割技术有望成为放射科和骨科医生的标准辅助工具,为患者提供更精准的诊疗服务。
参考文献
Ronneberger O, Fischer P, Brox T. U-net: Convolutional networks for biomedical image segmentation. MICCAI 2015.
Çiçek Ö, et al. 3D U-Net: learning dense volumetric segmentation from sparse annotation. MICCAI 2016.
Lessmann N, et al. Deep learning-based regression and classification for automatic landmark localization in medical images. IEEE TMI 2020.
Janssens R, et al. Fully automatic segmentation of lumbar vertebrae from CT images using cascaded 3D fully convolutional networks. ISBI 2018.
Liao H, et al. Automatic lumbar spine segmentation using a shape-aware multi-task network. MICCAI 2019.